Page 11 - 88_01
P. 11
ANALES
RANF
www.analesranf.com
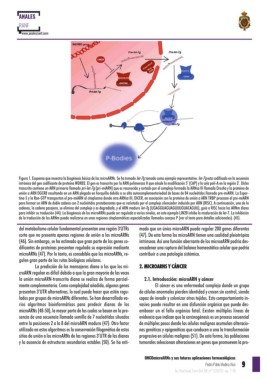
Figura 1. Esquema que muestra la biogénesis básica de los microARNs. Se ha tomado let-7g tomado como ejemplo representativo. let-7g esta codificado en la secuencia
intrónica del gen codificante de proteína WDR82. El gen es transcrito por la ARN polimerasa II que añade la modificación 5’ (CAP) y la cola poli-A en la región 3’. Dicho
transcrito contiene un ARN primario llamado pri-let-7g (pri-miARN) que es reconocido y cortado por el complejo formado la ARNsa III llamada Drosha y la proteína de
unión a ARN DGCR8 resultando en un ARN plegado en horquilla debido a su alta autocomplementariedad de bases de 84 nucleótidos llamado pre-miARN. La Expor-
tina-5 y la Ran-GTP transportan el pre-miARN al citoplasma donde otra ARNsa III, DICER, en asociación con la proteína de unión a ARN TRBP procesan al pre-miARN
para formar un ARN de doble cadena con 2 nucleótidos protuberantes que es reclutado por el complejo silenciador inducido por ARN (RISC). A continuación, una de la
cadenas, la cadena pasajera, se elimina del complejo y es degradada, y el ARN maduro let-7g (UGAGGUAGUAGUUUGUACAGUU), guía a RISC hacia los ARNm diana
para inhibir su traducción (44). La biogénesis de los microARNs puede ser regulada a varios niveles, en este ejemplo LIN28 inhibe la maduración de let-7. La inhibición
de la traducción de los ARNm puede realizarse en unas regiones citoplasmáticas especializadas llamados cuerpos P (ver el texto para detalles adicionales). (45).
del metabolismo celular fundamental presentan una región 3'UTRs mado que un único microARN puede regular 200 genes diferentes
corta que no presenta apenas regiones de unión a los microARNs (47). De esta forma los microARN tienen una cualidad pleiotrópica
(46). Sin embargo, se ha estimado que gran parte de los genes co- intrínseca. Así una función aberrante de los microaARN podría des-
dificantes de proteínas presentan regulada su expresión mediante encadenar una ruptura del balance homeostático celular que podría
microARNs (47). Por lo tanto, es concebible que los microARNs, re- contribuir a una patología sistémica.
gulen gran parte de las rutas biológicas celulares. 2. MICROARNS Y CÁNCER
La predicción de los mensajeros diana a los que los mi- 2.1. Introducción: microARN y cáncer
croARN regulan es difícil debido a que la gran mayoría de las veces El cáncer es una enfermedad compleja donde un grupo
la unión microARN-transcrito diana se realiza de forma parcial-
mente complementaria. Como complejidad añadida, algunos genes de células anormales pierden identidad y crecen sin control, siendo
presentan 3’UTR alternativas, lo cual puede hacer que estén regu- capaz de invadir y colonizar otros tejidos. Este comportamiento in-
lados por grupos de microARNs diferentes. Se han desarrollado va- vasivo puede resultar en una disfunción orgánica que puede des-
rios algoritmos bioinformáticos para predecir dianas de los embocar un el fallo orgánico fatal. Existen múltiples líneas de
microARNs (48-50), la mayor parte de los cuales se basan en la pre- evidencia que indican que la carcinogénesis es un proceso secuencial
sencia de una secuencia llamada semilla de 7 nucleótidos situados de múltiples pasos donde las células malignas acumulan alteracio-
entre la posiciones 2 a la 8 del microARN maduro (47). Otro factor nes genéticas y epigenéticas que conducen a una la transformación
utilizado en estos algoritmos es la conservación filogenética de estos progresiva en células malignas (51). De esta forma, las poblaciones
sitios de unión a los microARNs de las regiones 3’UTR de las dianas tumorales seleccionan alteraciones en genes que promueven la pro-
y la ausencia de estructuras secundarias estables (50). Se ha esti-
ONCOmicroARNs y sus futuras aplicaciones farmacológicas 9
Pedro Pablo Medina Vico
An. Real Acad. Farm.Vol. 88. nº 1 (2022) · pp. 7-18